Entstanden in einem Genetik-Labor. Gebaut fuer alles.
Zyrkel entstand am Institut fuer Humangenetik des UKE Hamburg. Das urspruengliche Problem war einfach: Genomik-Pipelines sind komplex, Parameter aendern sich zwischen Datensaetzen, SLURM-Jobs laufen um 3 Uhr nachts — und die meisten Studierenden und Forschenden koennen nicht programmieren. Bioinformatik-Tools sollten fuer alle im Labor zugaenglich sein, nicht nur fuer die eine Person die Python kann. Also wurde ein System gebaut, das diese Huerde auf Null senkt: Sag was du brauchst, und es erledigt den Rest. Es merkt sich jeden Parameter, jedes Ergebnis, jede gelernte Lektion.
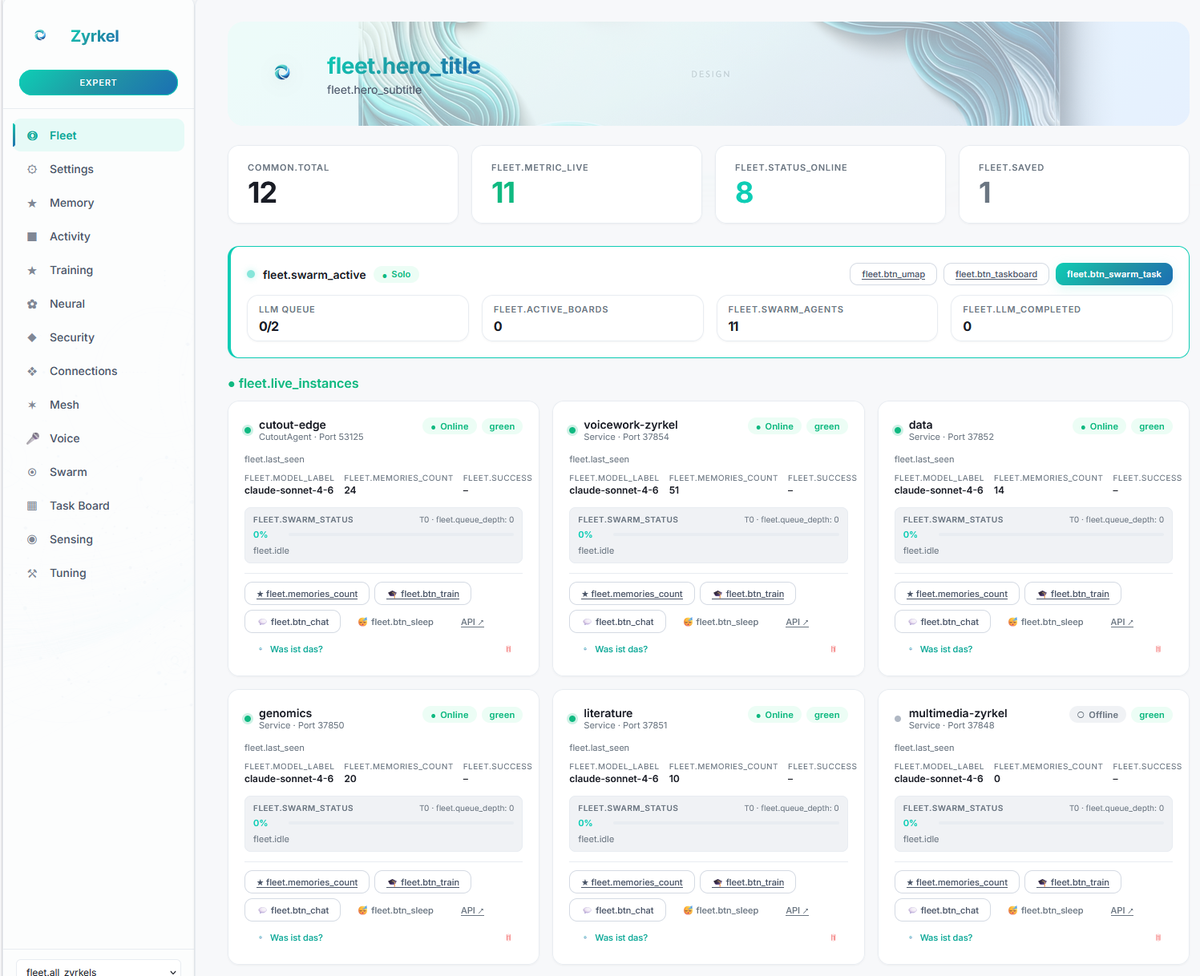
Dann generalisierte das Memory-System. Tools kamen dazu — nicht nur fuer Genomik, sondern fuer alles. Ein Desktop-Overlay erschien, das den Bildschirm lesen und im Kontext antworten konnte. Sprache folgte. Dann kam das Feature, das alles veraenderte: Docke einen Zyrkel an zwei Programme die keine gemeinsame API haben, und sie kommunizieren darueber. Dann kam das Fleet-System — aus einem Zyrkel wurden zwei, dann zehn, dann hunderte, jeder spezialisiert, jeder lernt unabhaengig, alle koordinieren sich.
Heute laeuft ein einzelnes 25MB Binary — oder eine Flotte von tausenden — auf deinem Laptop, deinem HPC-Cluster oder deiner Kubernetes-Infrastruktur. Es klassifiziert genetische Varianten und bearbeitet Excel-Tabellen. Es ueberwacht Heartbeats und schreibt E-Mails. Es generiert Ideen und fuehrt sie autonom aus. Es ist eine kognitive Einheit, die ueberall andockt wo sie gebraucht wird.