Né dans un laboratoire de génétique. Conçu pour tout.
Zyrkel a vu le jour à l'Institut de génétique humaine de l'UKE Hambourg. Le problème initial était simple : les pipelines de génomique sont complexes, les paramètres changent d'un jeu de données à l'autre, les jobs SLURM tournent à 3h du matin — et la plupart des étudiants et chercheurs ne savent pas coder. Les outils de bioinformatique devraient être accessibles à tous dans un laboratoire, pas seulement à la seule personne qui connaît Python. Un système a donc été créé pour réduire cette barrière à zéro : dites-lui ce dont vous avez besoin, et il s'occupe du reste. Il mémorise chaque paramètre, chaque résultat, chaque leçon apprise.
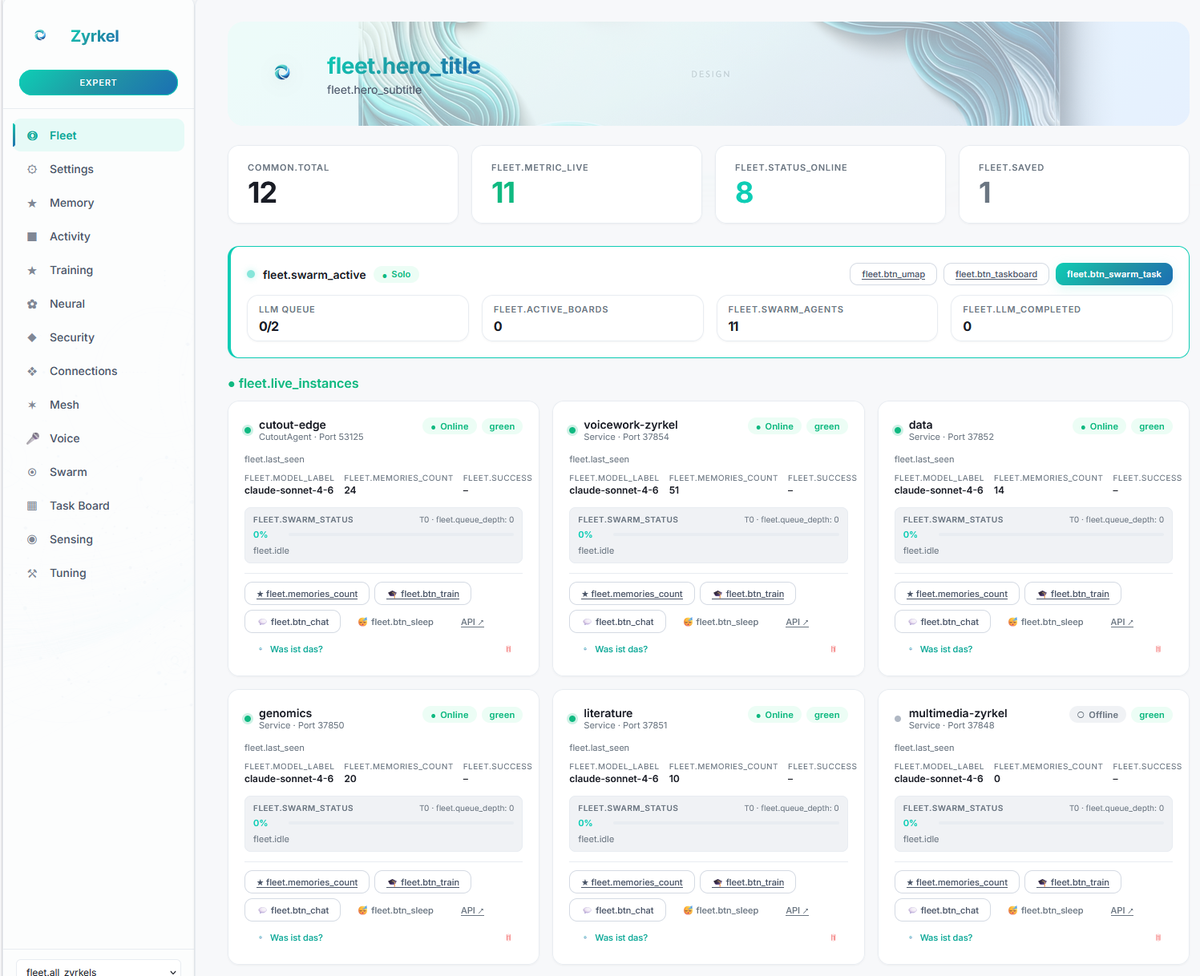
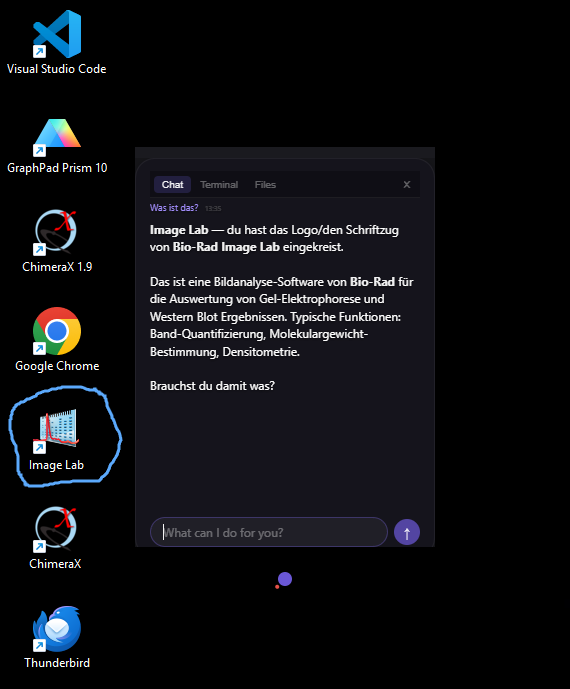
Puis le système de mémoire s'est généralisé. Des outils ont été ajoutés — pas seulement pour la génomique, mais pour tout. Une surcouche bureau est apparue, capable de lire l'écran et de répondre en contexte. La voix a suivi. Puis est venue la fonctionnalité qui a tout changé : arrimer un Zyrkel à deux programmes sans API commune, et ils communiquent à travers lui. Ensuite, le système de flotte est arrivé — un Zyrkel est devenu deux, puis dix, puis des centaines, chacun spécialisé, chacun apprenant de manière indépendante, tous se coordonnant.
Aujourd'hui, un seul binaire de 25 Mo — ou une flotte de milliers — tourne sur votre ordinateur portable, votre cluster HPC ou votre infrastructure Kubernetes. Il gère la classification de variants génomiques et les feuilles de calcul Excel. Il surveille les battements de cœur et rédige des e-mails. Il génère des idées et les exécute de manière autonome. C'est une unité cognitive qui s'arrime partout où elle est nécessaire.