Urodzony w laboratorium genetycznym. Zbudowany do wszystkiego.
Zyrkel powstał w Instytucie Genetyki Człowieka w UKE Hamburg. Problem był prosty: pipeline'y genomiczne są skomplikowane, parametry zmieniają się między zbiorami danych, zadania SLURM działają o 3 w nocy — a większość studentów i badaczy nie umie programować. Narzędzia bioinformatyczne powinny być dostępne dla każdego w laboratorium, nie tylko dla jednej osoby, która zna Python. Dlatego zbudowano system, który redukuje tę barierę do zera: powiedz mu, czego potrzebujesz, a on zajmie się resztą. Zapamiętuje każdy parametr, każdy wynik, każdą wyciągniętą lekcję.
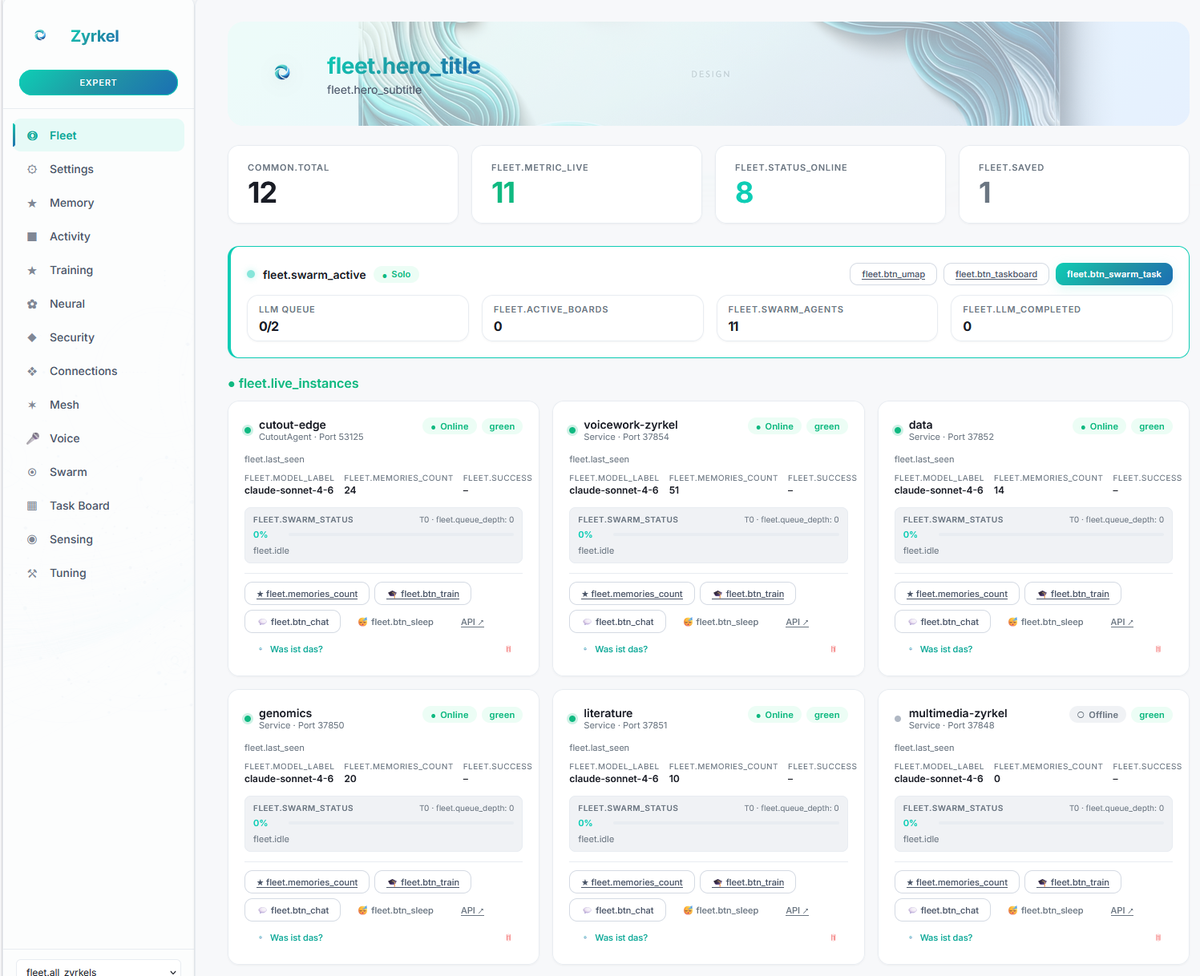
Potem system pamięci się uogólnił. Dodano narzędzia — nie tylko do genomiki, ale do wszystkiego. Pojawiła się nakładka na pulpit, która mogła czytać ekran i odpowiadać w kontekście. Doszedł głos. Potem przyszła funkcja, która zmieniła wszystko: zadokuj Zyrkel do dwóch programów bez wspólnego API, a komunikują się przez niego. Następnie nadszedł system floty — jeden Zyrkel stał się dwoma, potem dziesięcioma, potem setkami, każdy wyspecjalizowany, każdy uczący się niezależnie, wszystkie koordynujące się.
Dziś pojedynczy plik binarny o rozmiarze 25 MB — lub flota tysięcy — działa na twoim laptopie, klastrze HPC lub infrastrukturze Kubernetes. Obsługuje klasyfikację wariantów genomicznych i arkusze kalkulacyjne Excel. Monitoruje puls i pisze e-maile. Generuje pomysły i realizuje je autonomicznie. To jednostka kognitywna, która dokuje wszędzie tam, gdzie jest potrzebna.